博文
课程实例:分子对接-MOE入门简介
|
实例1的内容是基于前面讲述的分子力场进行分子对接的实践操作。
选用软件为MOE。MOE的界面操作比较简单,且会显示docking的过程,我认为比较适合教学展示。
选用体系为ATP和Remdesivir(REM)与新冠病毒的RNA聚合酶的分子对接,并简单比较两者与RNA聚合酶相互作用的异同。
1. 从蛋白质数据库(www.rscb.org)下载新冠病毒的RNA聚合酶的结构文件(pdb id: 7bv2),并在MOE中打开(File→open)。

可以看到这个结构中RNA聚合酶的活性位点中有REM分子,不过REM已经添加到RNA末端,有PPi(PYROPHOSPHATE)。
2. 处理蛋白(右侧的QuickPrep)。

这一步主要是补全缺失的侧链、加氢、质子化等。
3. 加载ATP和REM分子(之前课程中介绍ChemDraw时绘制的分子结构,mol2格式)(File→open)。点击下方的2D可以查看小分子的分子式。

4. 分子对接(Compute→dock)。

Poses中的30和5意思为共生成30个构象(poses),根据打分列出前5个,可以根据需要修改,我们这里就选用默认值30和5。refinement分别用Rigid Receptor和induced fit做两组对接,比较两种情况下得到的结构的异同。注意修改output文件名。
点击run之后,工作框会显示docking的过程,小分子的构象采样过程,在refinement选用induced fit的时候也是显示周围蛋白质残基的采样过程。打开上方的SVL会显示dock过程的进程。

5. 结果查看。结果会显示在Database Viewer中(三个底物,每个显示5个poses),其中包括打分、RMSD等。
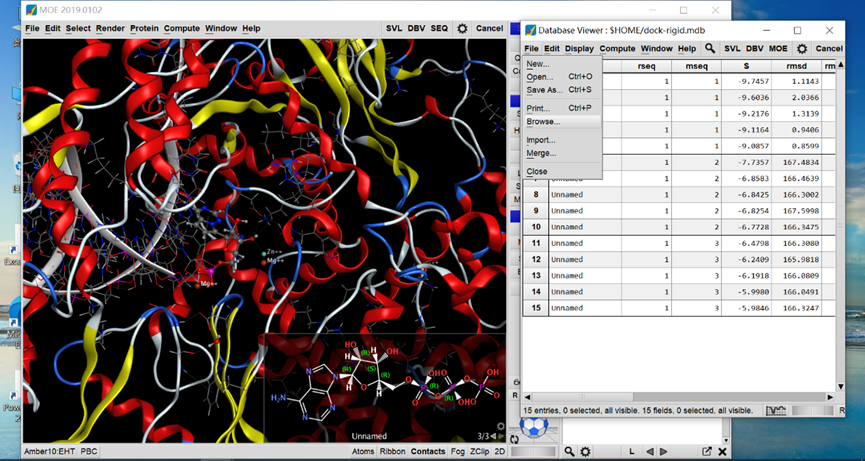
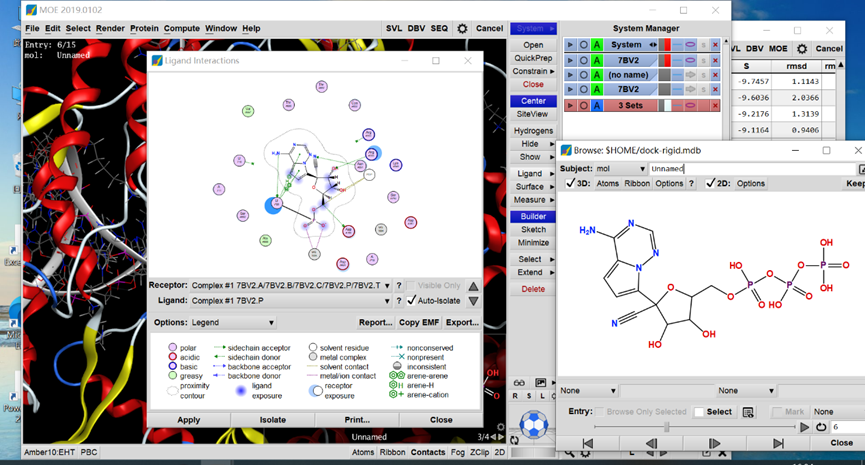
具体结构可以通过Database Viewer中File→Browse查看。通过右侧的Ligand→ligand interactions可以查看每一个pose中ligand与蛋白的具体相互作用情况,如下图。
https://m.sciencenet.cn/blog-3375255-1341565.html
上一篇:一堂充满遗憾的课
下一篇:有些伤害真的是深入骨髓的
全部作者的精选博文
- • 写给大一新生---大学学习方法之我见II
- • 汉语,我唯一的行囊
- • 写给大一新生---大学学习方法之我见I
- • 优秀是一种习惯
- • 科技论文简介
- • 写邮件